Mundo
Por que simular um ciclo celular completo levou anos, várias GPUs e seis dias por execução?
A equipe simulou uma célula viva em resolução nanométrica e reproduziu o comportamento de cada molécula dentro dessa célula ao longo de um ciclo celular completo.
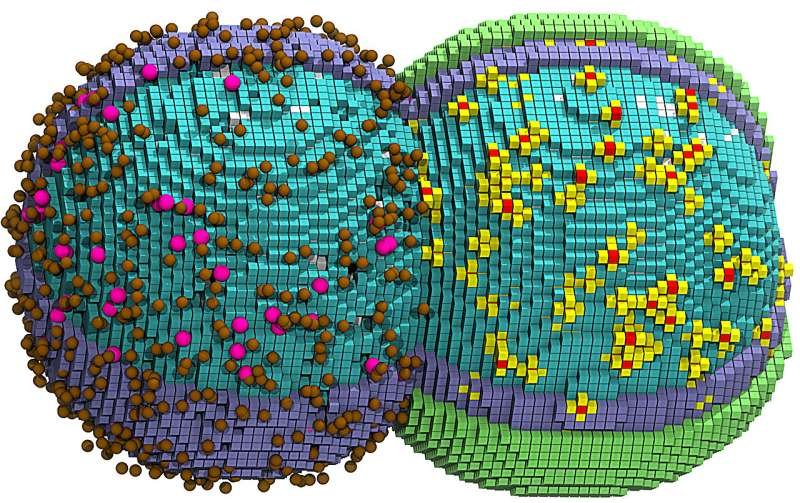
Uma célula simulada nos estágios iniciais de divisão. A metade esquerda mostra o citoplasma (cubos azuis), moléculas da maquinaria de degradação do mRNA (rosa) e transportadores de açúcar (marrom). A metade direita adiciona a membrana (verde) e os ribossomos (amarelo/vermelho). Crédito: Zane Thornburg, Cell . DOI: 10.1016/j.cell.2026.02.009.
Ao simular o ciclo de vida de uma célula bacteriana mínima — da replicação do DNA à tradução de proteínas, passando pelo metabolismo e divisão celular — cientistas abriram uma nova fronteira da visão computacional nos processos essenciais da vida. Os pesquisadores, liderados pelo professor de química Zan Luthey-Schulten, da Universidade de Illinois em Urbana-Champaign, apresentam suas descobertas na revista Cell .
A equipe simulou uma célula viva em resolução nanométrica e reproduziu o comportamento de cada molécula dentro dessa célula ao longo de um ciclo celular completo. O trabalho levou muitos anos: vastos recursos computacionais, grandes conjuntos de dados experimentais, uma gama de técnicas experimentais e computacionais e uma compreensão dos papéis, comportamentos e interações físicas de milhares de moléculas.
Os pesquisadores tiveram que levar em conta cada gene, proteína, molécula de RNA e reação química que ocorre dentro da célula para recriar a sequência de eventos celulares. Por exemplo, seu modelo precisava refletir com precisão os processos que permitem que a célula dobre de tamanho antes da divisão celular.
Para tornar a tarefa mais gerenciável, a equipe utilizou uma "célula mínima" viva desenvolvida no Instituto J. Craig Venter, na Califórnia. A versão da célula usada no novo estudo, JCVI-syn3A — ou simplesmente "Syn3A" —, é uma bactéria modificada com um genoma reduzido que carrega apenas os genes necessários para replicar seu DNA, crescer, se dividir e realizar a maioria das outras funções que tornam a vida possível.
"Este é um modelo cinético tridimensional e totalmente dinâmico de uma célula viva mínima que imita o que acontece na célula real", disse Luthey-Schulten.
"Um empreendimento tão abrangente só foi possível graças aos esforços conjuntos de diversos colaboradores da Universidade de Illinois e da Escola de Medicina de Harvard, onde modelamos sistematicamente o metabolismo essencial e outras redes subcelulares por meio de uma série de publicações iniciadas em 2018."
Uma célula simulada nos estágios iniciais de divisão. A metade esquerda mostra a membrana (cubos verdes) e os ribossomos (amarelos/roxos) entrelaçados no cromossomo da célula (vermelho). O lado direito mostra todas as proteínas (cinza) e o RNA (laranja) dentro da célula, com um pequeno corte transversal para mostrar uma segunda cópia do cromossomo da célula (azul). Crédito: Zane Thornburg. Cell . DOI: 10.1016/j.cell.2026.02.009.
Construindo e validando a célula mínima
A célula Syn3A possui menos de 500 genes, todos localizados em uma única fita circular de DNA. Os laboratórios dos coautores do estudo, Angad Mehta, professor de química na Universidade de Illinois, e Taekjip Ha, do Hospital Infantil de Boston e da Escola de Medicina de Harvard, geraram dados experimentais adicionais que permitiram à equipe simular e validar com precisão diversos aspectos da função celular.
"Mais importante ainda, o trabalho deles revelou a extensão da replicação do DNA e que a divisão celular da Syn3A é simétrica", disse Luthey-Schulten.
Ambos os fatores orientaram e validaram as simulações realizadas por Zane Thornburg, um pós-doutorando do Instituto Beckman de Ciência e Tecnologia Avançadas e do Centro de Câncer de Illinois, e por Andrew Maytin, um estudante de pós-graduação no laboratório de Luthey-Schulten.
Assim como outras células bacterianas, a Syn3A não possui núcleo. Todas as moléculas que a compõem e a sustentam são componentes de sua membrana externa, são transportadas para dentro da célula a partir do exterior ou são sintetizadas no citoplasma.
A célula é tão repleta de componentes moleculares que, ao criar animações e representações em alta resolução de suas simulações computacionais, os pesquisadores tiveram que tornar alguns desses componentes invisíveis. Tornar todas as proteínas celulares invisíveis, por exemplo, permitiu aos cientistas observar como o cromossomo da Syn3A se move pelo interior denso da célula.
A equipe descobriu que alguns processos eram mais dispendiosos computacionalmente do que outros. Por exemplo, Maytin percebeu que a replicação dos cromossomos estava tornando toda a simulação extremamente lenta, quase dobrando o tempo necessário para capturar todo o ciclo celular.
Ele determinou que a simulação eficiente do processo de replicação do DNA da célula exigia uma unidade de processamento gráfico dedicada, enquanto outra GPU lidava com todas as outras dinâmicas celulares. Isso permitiu que a equipe simulasse o ciclo celular completo de 105 minutos em apenas seis dias de tempo de computador.
Superando os obstáculos da simulação 3D
Thornburg e Maytin enfrentaram o desafio de simular eventos celulares que ocorrem simultaneamente em várias partes da célula.
"Não consigo enfatizar o quão difícil é simular coisas em movimento — e fazer isso em 3D para uma célula inteira foi... triunfante", disse Thornburg. "Um dos últimos grandes obstáculos que Andrew e eu tivemos que superar foi entender como a membrana e o DNA se comunicam quando ambos estão em movimento."
Embora o ciclo celular simulado tenha suas limitações — não se tratava de uma simulação átomo por átomo, mas sim de uma média da dinâmica de moléculas individuais —, ele produziu um relato surpreendentemente preciso da cronologia dos processos celulares.
Em simulações repetidas envolvendo células individuais com condições iniciais ligeiramente variáveis, o ciclo celular simulado ocorreu, em média, dentro de dois minutos do ciclo celular real, disse Thornburg. O trabalho foi repetidamente orientado e testado em comparação com resultados experimentais reais, um processo que permitiu aos cientistas refinar suas simulações.
Uma nova janela para os sistemas vivos
A capacidade de capturar com precisão as condições em constante mudança dentro de uma célula viva abre uma nova janela para os fundamentos dos sistemas vivos, disse Luthey-Schulten.
"Temos um modelo de célula inteira que prevê muitas propriedades celulares simultaneamente", disse ela. "Se você quiser saber o que está acontecendo, digamos, no metabolismo de nucleotídeos, também pode observar o que está acontecendo na replicação do DNA e na biogênese dos ribossomos. Assim, as simulações podem fornecer os resultados de centenas de experimentos simultaneamente."
Entre os coautores do estudo estão Benjamin Gilbert, ex-aluno de química da Universidade de Illinois, e John Glass, que lidera o Grupo de Biologia Sintética do Instituto J. Craig Venter.
Este trabalho foi realizado no Centro de Ciência e Tecnologia para Biologia Celular Quantitativa da Fundação Nacional de Ciência (NSF) da Universidade de Illinois (U. of I.). Luthey-Schulten também é professora de física e professora do Instituto Beckman da U. of I. A pesquisa foi conduzida utilizando o recurso avançado de computação e dados Delta. O Delta é um projeto conjunto da U. of I. e seu Centro Nacional de Aplicações de Supercomputação.
Detalhes da publicação
Dando vida à célula geneticamente mínima em um computador em 4D, Cell (2026). DOI: 10.1016/j.cell.2026.02.009 . www.cell.com/cell/fulltext/S0092-8674(26)00174-1
Informações do periódico: Célula